SVD (SVD와 Latent Factor 모형)
이해하기 쉽고, 장황하지 않은 자료를 기반으로 강의를 진행합니다.
6. SVD (SVD와 Latent Factor 모형)¶
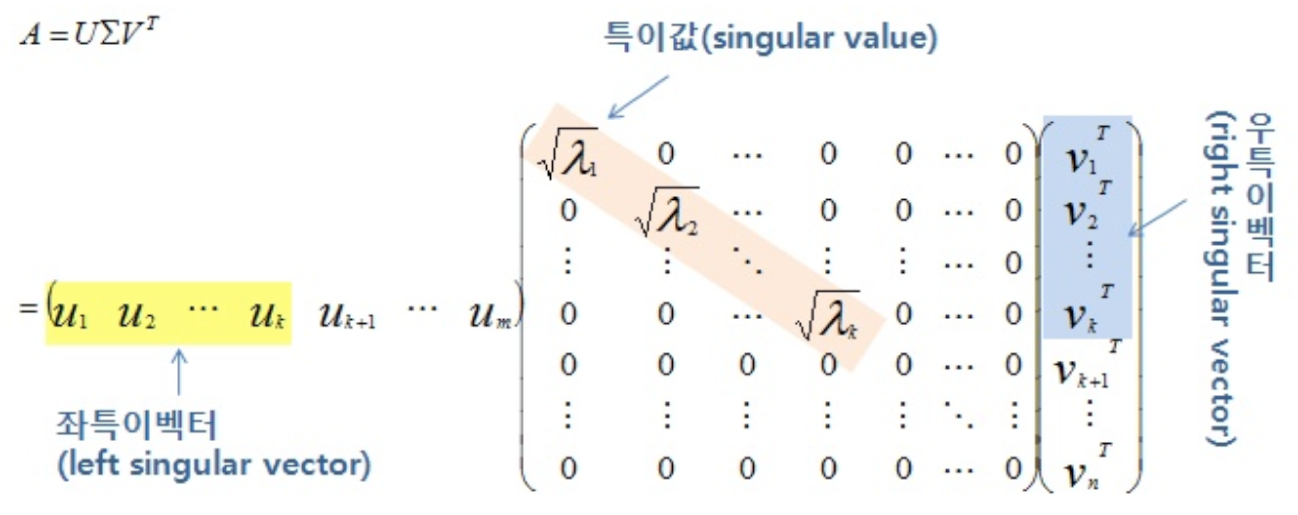
정방 행렬 ($n x n$) $A$에 대한 다음 식에서
$$ Av = \lambda v $$$ A \in \mathbf{R}^{M \times M} $
$ \lambda \in \mathbf{R} $
$ v \in \mathbf{R}^{M} $
위 식을 만족하는 실수 $\lambda$를 고유값(eigenvalue)
단위 벡터 $v$ 를 고유벡터(eigenvector)
라고 하며, 이를 고유 분해라고 함
- 정방 행렬이 아닌 행렬 $M$에 대해서도 고유 분해와 유사한 분해가 가능
- 이를 특이값 분해(singular value decomposition)이라고 함
- $m \times n$ 크기의 행렬 $R$은 다음과 같이 세 행렬의 곱으로 나타낼 수 있음</p>
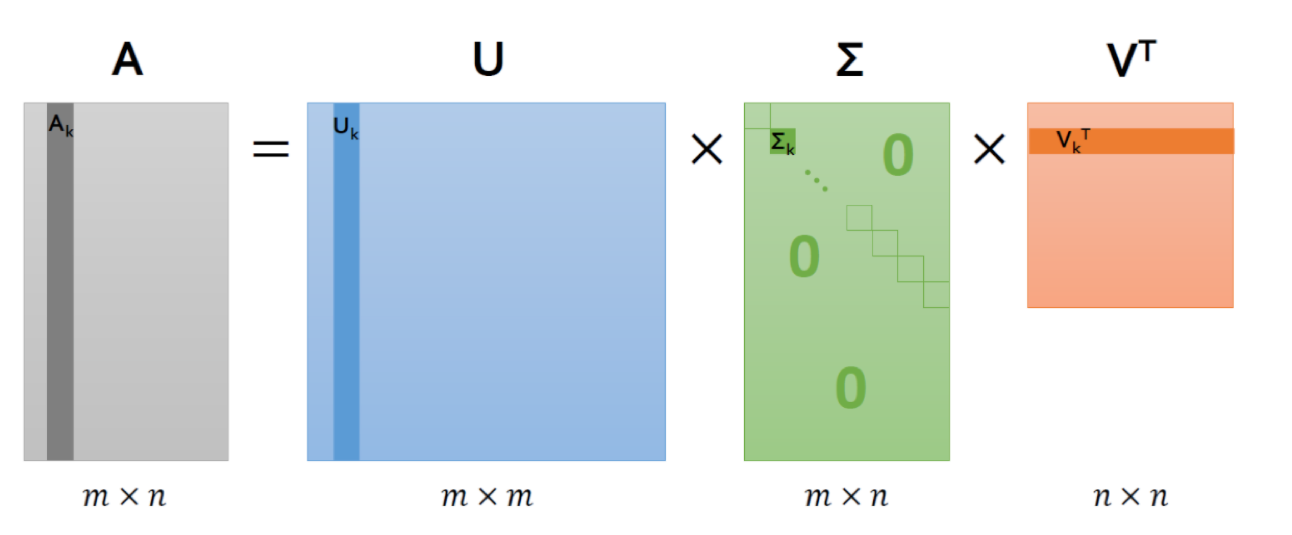
$$ R = U \Sigma V^T $$
이 식에서
SVD은 R 과 RT 의 PCA¶
- 사용자 요인 벡터와 영화 요인 벡터로 사용자/영화별 평점 행렬의 요인 벡터로 분리하자!
SVD 증명
- A를 ($m x n$) 행렬이라 할때
- $AA^T 는 정방행렬(n x n 행렬)이 되고$
- $AA^T = Q \Lambda Q^T 와 같이 분해될 수 있음$
- 이 때, $Q$:고유벡터를 열로 가지는 행렬, $\Lambda$:고유값으로 채워진 대각행렬
- A는 SVD에 의해 $U \Sigma V^T$ 로 분해 가능
- 그렇다면, $AA^T$ = $Q \Lambda Q^T$
- 이 때 역시, $Q$:고유벡터를 열로 가지는 행렬, $\Lambda$:고유값으로 채워진 대각행렬
- SVD 수식을 사용하면,
- $AA^T = (U\Sigma V^T)(U\Sigma V^T)^T = (U\Sigma V^T)(V\Sigma^T U^T) = U(\Sigma \Sigma^T)U^T$
- $A^TA = (U\Sigma V^T)^T(U\Sigma V^T) = (V\Sigma^T U^T)(U\Sigma V^T) = V(\Sigma^T \Sigma)V^T$
- V 와 U 는 직교행렬(orthogonal matrix) 특성을 가지므로, $U^T U = I$ $V^T V = I$
- 다시 행렬 A의 공분산 행렬 식을 보면,
$$\begin{align*} \Sigma =cov(A)&= \frac{1}{n-1} \sum_{i=1}^n (A_i-\mu)(A_i-\mu)^T = \frac { 1 }{ n-1 } A { A^T } \propto A A^T\\\\ \end{align*}$$ - $U$는 $AA^T$ 즉, $A$의 공분산 행렬의 고유벡터
- $V$는 $A^T A$ 즉, $A^T$의 공분산 행렬의 고유벡터
- $\Sigma \Sigma^T$ 또는 $\Sigma^T \Sigma = \lambda$
- 따라서, singular value (특이값) $σ$ = $\sqrt{\lambda}$
- 다시 행렬 A의 공분산 행렬 식을 보면,
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
퀄러티가 다른 온라인 강의로 차근차근 익혀보세요
- $\Sigma$ 는 공분산 행렬의 고유값의 제곱근(루트)
$\begin{align*} { A }^{ T }A&={ (U\Sigma { V }^{ T }) }^{ T }U\Sigma { V }^{ T }\\ &=V\Sigma { U }^{ T }U\Sigma { V }^{ T }\\ &=V{ \Sigma }^{ 2 }{ V }^{ T }\\ &=V\Lambda { V }^{ T } \end{align*}$
다시 정리 하는 SVD¶
- 정방행렬이 아닌 A 행렬 (m x n) 에 대해
- $U: AA^T$의 고유벡터 (m x m)
- $\Sigma : A$의 특이값들을 대각항으로 가지는 대각행렬 (m x n)
- 특이값(singular value)은 $AA^T 와 A^T A$의 고유값의 제곱근
- $V: A^T A$의 고유벡터 (n x n)
SVD은 $A$ 와 $A^T$ 의 PCA¶
- $ U \Sigma V^T $ 에서 $ \Sigma $ 는 대각행렬로 $ U 와 V^T $의 중복 고유값의 제곱으로 scaler 역할이 됨
- 따라서, A 행렬 = $U$ $V^T$ 로 행렬 인수분해한 모델로 가정할 수 있음
- $U$는 X (사용자 수 x k) 인 사용자 특징(요인) 행렬
- $\Sigma V^T$는 Y (영화 수 x k) 인 영화 특징(요인) 행렬
- $\Sigma$ 은 scale에 관련된 값이므로 특별히 특징 행렬로 큰 그림을 그릴시에는 무시해도 됨
이를 좀더 모델로 구체화하면¶
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
퀄러티가 다른 온라인 강의로 차근차근 익혀보세요
$$ r_{ui} = p_u \cdot q_i $$
- $p_u$: $U$의 한 행으로 사용자 요인을 나타냄
- $q_u$: $V^T$의 한 열로 영화 요인을 나타냄
사용자의 요인을 벡터화¶
\begin{array}{ll}
\text{Alice} & = 10\% \color{#048BA8}{\text{ Action fan}} &+ 10\%
\color{#048BA8}{\text{ Comedy fan}} &+
50\% \color{#048BA8}{\text{ Romance fan}} &+\cdots\\
\text{Bob} &= 50\% \color{#048BA8}{\text{ Action fan}}& + 30\%
\color{#048BA8}{\text{ Comedy fan}} &+ 10\%
\color{#048BA8}{\text{ Romance fan}} &+\cdots\\
\text{Titanic} &= 20\% \color{#048BA8}{\text{ Action}}& + 00\%
\color{#048BA8}{\text{ Comedy}} &+
70\% \color{#048BA8}{\text{ Romance}} &+\cdots\\
\text{Toy Story} &= 30\% \color{#048BA8}{\text{ Action }} &+ 60\%
\color{#048BA8}{\text{ Comedy}}&+ 00\%
\color{#048BA8}{\text{ Romance}} &+\cdots\\
\end{array}
\begin{align*}
p_\text{Alice} &= (10\%,~~ 10\%,~~ 50\%,~~ \cdots)\\
p_\text{Bob} &= (50\%,~~ 30\%,~~ 10\%,~~ \cdots)\\
q_\text{Titanic} &= (20\%,~~ 00\%,~~ 70\%,~~ \cdots )\\
q_\text{Toy Story} &= (30\%,~~ 60\%,~~00\%,~~ \cdots )
\end{align*}
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
퀄러티가 다른 온라인 강의로 차근차근 익혀보세요
\begin{align*}
r_{ui}= p_u \cdot q_i = \sum_{f \in \text{latent factors}} \text{affinity of } u
\text{ for } f \times \text{affinity of } i \text{ for }f
\end{align*}
In [ ]:
import numpy as np
from numpy import linalg as la
np.random.seed(42)
def flip_signs(A, B):
"""
utility function for resolving the sign ambiguity in SVD
http://stats.stackexchange.com/q/34396/115202
"""
signs = np.sign(A) * np.sign(B)
return A, B * signs
# Let the data matrix X be of n x p size,
# where n is the number of samples and p is the number of variables
n, p = 5, 3
X = np.random.rand(n, p)
# Let us assume that it is centered
# 평균이 0으로 맞춘 후에 (centering 작업 수행) 공분산 행렬을 계산함
X -= np.mean(X, axis=0)
# the p x p covariance matrix
C = np.cov(X, rowvar=False)
print ("covariance matrix = \n", C)
# C is a symmetric matrix and so it can be diagonalized:
l, principal_axes = la.eig(C)
# sort results wrt. eigenvalues
idx = l.argsort()[::-1]
l, principal_axes = l[idx], principal_axes[:, idx]
# the eigenvalues in decreasing order
print ("eigenvalues = \n", l)
# a matrix of eigenvectors (each column is an eigenvector)
print ("eigenvectors = \n", principal_axes)
# projections of X on the principal axes are called principal components
principal_components = X.dot(principal_axes)
print ("principal_components = \n", principal_components)
# we now perform singular value decomposition of X
# "economy size" (or "thin") SVD
U, s, Vt = la.svd(X, full_matrices=False)
V = Vt.T
S = np.diag(s)
# 1) then columns of V are principal directions/axes.
print ("V = \n", V)
assert np.allclose(*flip_signs(V, principal_axes))
# 2) columns of US are principal components
print ("US = \n", U.dot(S))
assert np.allclose(*flip_signs(U.dot(S), principal_components))
# 3) singular values are related to the eigenvalues of covariance matrix
print ((s ** 2) / (n - 1))
assert np.allclose((s ** 2) / (n - 1), l)
# 8) dimensionality reduction
k = 2
PC_k = principal_components[:, 0:k]
US_k = U[:, 0:k].dot(S[0:k, 0:k])
print (US_k)
assert np.allclose(*flip_signs(PC_k, US_k))
print (U)
print (S)
print (V)
# 10) we used "economy size" (or "thin") SVD
assert U.shape == (n, p)
assert S.shape == (p, p)
assert V.shape == (p, p)
특이값 분해 계산¶
In [183]:
import numpy as np
from pprint import pprint
import math
M = np.array([[math.sqrt(3), 2], [0, math.sqrt(3)]])
U, s, Vt = numpy.linalg.svd(M, full_matrices=True)
In [184]:
M
Out[184]:
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
체계적으로 전문가 레벨까지 익힐 수 있도록 온라인 강의 로드맵을 제공합니다
- $A^T A$ 의 고유값: $\lambda_1 = 9$, $\lambda_2 = 1$
- 특이값: $σ_1$ = $\sqrt{\lambda_1}$ = 3, $σ_2$ = $\sqrt{\lambda_2}$ = 1
- $\lambda_1 = 9$ 에 대응하는 $A^T A$의 단위고유벡터는 $v_1 = \begin{pmatrix} \frac{1}{2} \\ \frac{\sqrt{3}}{2} \end{pmatrix}$
- $\lambda_2 = 1$ 에 대응하는 $A^T A$의 단위고유벡터는 $v_2 = \begin{pmatrix} -\frac{\sqrt{3}}{2} \\ \frac{1}{2} \end{pmatrix}$
- $u_1 = \frac{1}{σ_1}Av_1 = \begin{pmatrix} \frac{\sqrt{3}}{2} \\ \frac{1}{2} \end{pmatrix}$
- $u_2 = \frac{1}{σ_2}Av_2 = \begin{pmatrix} -\frac{1}{2} \\ \frac{\sqrt{3}}{2} \end{pmatrix}$
- $U = [u_1, u_2] = \begin{pmatrix} \frac{\sqrt{3}}{2} \ -\frac{1}{2} \\ \frac{1}{2} \ \frac{\sqrt{3}}{2} \end{pmatrix}$
In [185]:
U
Out[185]:
- $V^T = [v_1, v_2] = \begin{pmatrix} \frac{1}{2} \ \frac{\sqrt{3}}{2} \\ -\frac{\sqrt{3}}{2} \ \frac{1}{2}\end{pmatrix}$
In [186]:
Vt
Out[186]:
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
체계적으로 전문가 레벨까지 익힐 수 있도록 온라인 강의 로드맵을 제공합니다
$ \Sigma = \begin{pmatrix} 3 \ 0 \\ 0 \ 1 \end{pmatrix}$
In [192]:
np.diag(s)
Out[192]:
$ U \Sigma V^T = \begin{pmatrix} \frac{\sqrt{3}}{2} \ -\frac{1}{2} \\ \frac{1}{2} \ \frac{\sqrt{3}}{2} \end{pmatrix} \begin{pmatrix} 3 \ 0 \\ 0 \ 1 \end{pmatrix}\begin{pmatrix} \frac{1}{2} \ \frac{\sqrt{3}}{2} \\ -\frac{\sqrt{3}}{2} \ \frac{1}{2}\end{pmatrix}$
In [197]:
U.dot(np.diag(s)).dot(Vt)
Out[197]:
In [199]:
import numpy as np
from pprint import pprint
M = np.array([[1,0,0,0,0],[0,0,2,0,3],[0,0,0,0,0],[0,2,0,0,0]])
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
퀄러티가 다른 온라인 강의로 차근차근 익혀보세요
In [200]:
U, S0, V0 = np.linalg.svd(M, full_matrices=True)
In [201]:
M
Out[201]:
In [202]:
U
Out[202]:
In [203]:
S0
Out[203]:
In [204]:
S = np.hstack([np.diag(S0), np.zeros(M.shape[0])[:, np.newaxis]])
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
퀄러티가 다른 온라인 강의로 차근차근 익혀보세요
In [205]:
S
Out[205]:
In [144]:
V = V0.T
In [145]:
V
Out[145]:
In [148]:
print("\nU.dot(S).dot(V.T):"); pprint(U.dot(S).dot(V0))
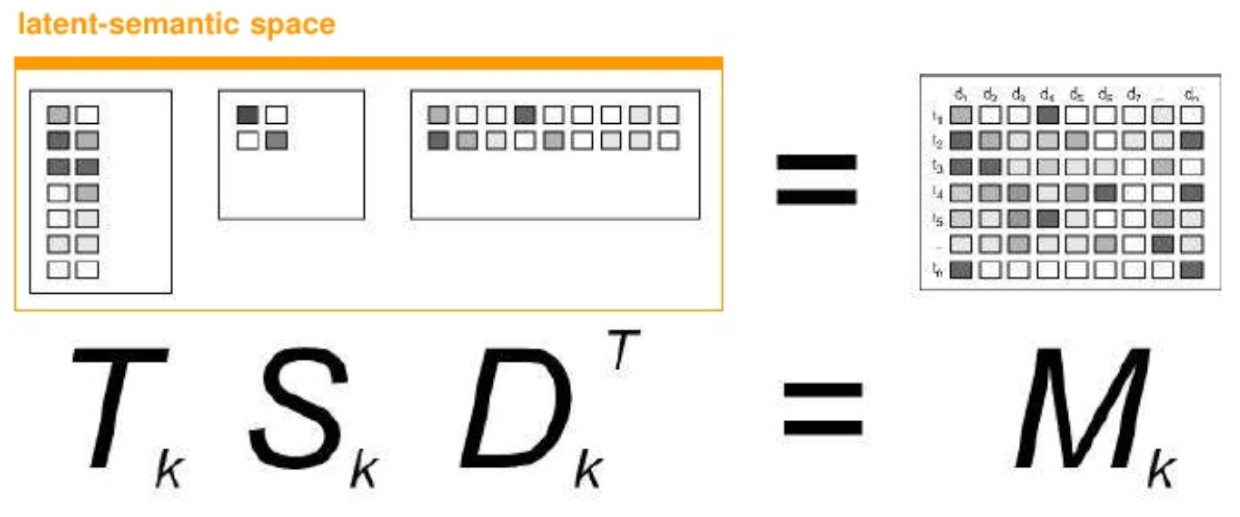
Trancated SVD: S에서 고유값 제곱이 0인 부분들을 없애면 차원 축소가 가능하고, 계산량을 줄일 수 있음¶
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
퀄러티가 다른 온라인 강의로 차근차근 익혀보세요
계산량 축소 $\lambda > 0$ 인 것만 사용하기¶

In [206]:
S
Out[206]:
sklearn의 TruncatedSVD 사용 예¶
In [78]:
from sklearn.decomposition import TruncatedSVD
from sklearn.random_projection import sparse_random_matrix
X = sparse_random_matrix(5, 5)
svd = TruncatedSVD(n_components=2, n_iter=7)
U = svd.fit_transform(X)
Sigma = svd.explained_variance_ratio_
VT = svd.components_
svd.fit(X)
Out[78]:
In [79]:
U
Out[79]:
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
체계적으로 전문가 레벨까지 익힐 수 있도록 온라인 강의 로드맵을 제공합니다
- 나머지 singular vector value는 0이기 때문에 삭제한다.
In [80]:
Sigma
Out[80]:
In [81]:
VT
Out[81]:
- 본래 U는 5X5, Sigma는 5X5, $V^T$는 5X5
- Truncated SVD로 변환: U는 5X2, Sigma는 2X2, $V^T$는 2X5
그러나, 사실 PCA, SVD는 dense matrix에서나 가능한 예!¶
- SVD는 dense matrix인 이미지의 차원축소에 많이 사용됨
- 사용자/영화의 평점 행렬은 평점이 많지 않은 sparse 행렬임!
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
체계적으로 전문가 레벨까지 익힐 수 있도록 온라인 강의 로드맵을 제공합니다
어떻게 sparse 행렬인 사용자/영화 평점 행렬에 SVD를 사용할까?¶
- 초기 $p_u$, $q_u$를 임의로 정하고, 이를 이용해서 근사 행렬 $Q$를 구한다.
$$ r_{ui} = p_u \cdot q_i $$
- $p_u$: $U$의 한 행으로 사용자 요인을 나타냄
- $q_u$: $V^T$의 한 열로 영화 요인을 나타냄
어떻게 사용자, 영화 특징(요인)으로부터 계산된 예측 평점의 정확도를 높일 것인가?¶
- $r_{ui}$ 를 $Q$라 하고, 실제 평점 $R$과의 차이를 손실 함수로 만들자
- min($R$ - $Q$)
sparse matrix인 평점 행렬에 대해 SGD를 사용한 실제 SVD 구현 예¶
In [44]:
import numpy as np
import surprise # run 'pip install scikit-surprise' to install surprise
In [47]:
class SVD_SGD(surprise.AlgoBase):
def __init__(self, learning_rate, n_epochs, n_factors):
self.lr = learning_rate # learning rate for SGD
self.n_epochs = n_epochs # number of iterations of SGD
self.n_factors = n_factors # number of factors (몇 개의 Latent Factor로 요인 벡터를 만들지를 정함)
def train(self, trainset):
'''Learn the vectors p_u and q_i with SGD'''
print('Fitting data with SGD...')
# Randomly initialize the user and item factors.
p = np.random.normal(0, .1, (trainset.n_users, self.n_factors))
q = np.random.normal(0, .1, (trainset.n_items, self.n_factors))
# SGD procedure
for _ in range(self.n_epochs):
for u, i, r_ui in trainset.all_ratings():
err = r_ui - np.dot(p[u], q[i])
# Update vectors p_u and q_i
p[u] += self.lr * err * q[i]
q[i] += self.lr * err * p[u]
# Note: in the update of q_i, we should actually use the previous (non-updated) value of p_u.
# In practice it makes almost no difference.
self.p, self.q = p, q
self.trainset = trainset
def estimate(self, u, i):
'''Return the estmimated rating of user u for item i.'''
# return scalar product between p_u and q_i if user and item are known,
# else return the average of all ratings
if self.trainset.knows_user(u) and self.trainset.knows_item(i):
return np.dot(self.p[u], self.q[i])
else:
return self.trainset.global_mean
본 자료와 같이 IT 기술을 잘 정리하여, 온라인 강의로 제공하고 있습니다
퀄러티가 다른 온라인 강의로 차근차근 익혀보세요
In [48]:
# data loading. We'll use the movielens dataset (https://grouplens.org/datasets/movielens/100k/)
# it will be downloaded automatically.
data = surprise.Dataset.load_builtin('ml-100k')
data.split(2) # split data for 2-folds cross validation
In [49]:
algo = SVD_SGD(learning_rate=.01, n_epochs=10, n_factors=10)
surprise.evaluate(algo, data, measures=['RMSE'])
Out[49]:
베이스라인 모형(baseline model)을 사용해서 sparse 행렬에 미리 값을 넣은 후에 SGD를 돌리는 방식도 가능¶
- 사용자 아이디 $u$, 상품 아이디 $i$, 두 개의 카테고리 값 입력에서 평점 $r_{ui}$의 예측치 $\hat{r}_{ui}$ 을 예측하는 단순 모형
사용자와 상품 특성에 의한 평균 평점의 합으로 나타난다.</p> $$ \hat{r}_{ui} = \mu + b_u + b_i $$
$\mu$는 전체 평점의 평균
- $b_u$는 동일한 사용자에 의한 평점 평균값
- $b_i$는 동일한 상품에 대한 평점 평균값



